|

El bacalao de profundidad (Dissostichus eleginoides) pertenece a la clase Actinopterygii y al suborden Notothenioidei, que vive en aguas frías
NUEVO ESTUDIO | Información genómica sobre la merluza negra: un recurso para los estudios sobre peces antárticos
 MUNDIAL MUNDIAL
Monday, November 18, 2024, 01:00 (GMT + 9)
Un estudio reciente ha proporcionado un recurso fundamental para comprender el genoma de la merluza negra (Dissostichus eleginoides), conocida comúnmente como mero chileno. Este trabajo ofrece información genética valiosa sobre las diferencias y similitudes entre esta especie y los peces antárticos, en particular la merluza negra antártica (Dissostichus mawsoni), estrechamente relacionada con ella.
Descripción general de la especie
La merluza negra pertenece a la familia Nototheniidae y prospera en aguas frías y profundas del hemisferio sur, en particular alrededor de Sudamérica y las islas subantárticas. Este pez, que crece hasta dos metros de largo y vive hasta 50 años, se distingue por sus glicoproteínas anticongelantes únicas, que le permiten sobrevivir a temperaturas gélidas. La especie tiene un valor comercial significativo debido a su delicado sabor y textura firme, lo que la convierte en un manjar muy buscado. Sin embargo, la sobrepesca ha mermado gravemente las poblaciones, lo que ha posicionado a la especie como amenazada.
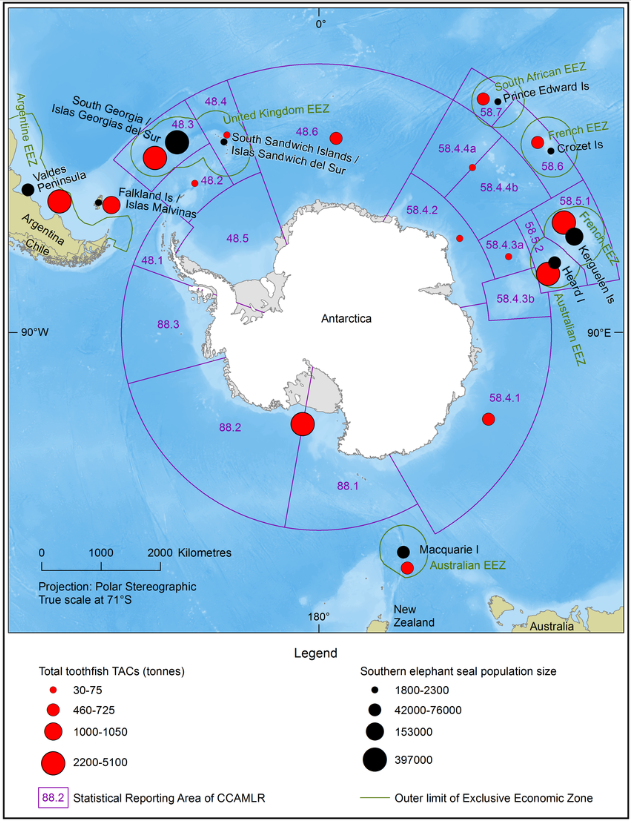
Capturas totales permisibles (CTP) de bacalao de profundidad (Dissostichus eleginoides) y estimaciones de población de elefante marino del sur (Mirounga leonina) Proyección polar del hemisferio sur que muestra los límites de la Comisión para la Conservación de los Recursos Vivos Marinos Antárticos (CCRVMA), las zonas económicas exclusivas (ZEE) nacionales, las CTP de bacalao de profundidad dentro de las regiones de la CCRVMA (burbujas rojas), las estimaciones de población de elefante marino del sur (burbujas negras) y la batimetría oceánica (sombreado azul; claro = poco profundo). Figura producida por el Centro Australiano de Datos Antárticos (c) Commonwealth of Australia 2016.Fuente: Researchgate
Análisis genómico comparativo
Este estudio exploró los rasgos genéticos y ecológicos que distinguen a la merluza negra patagónica y la merluza negra antártica. Por ejemplo, mientras que la merluza negra antártica alberga el gen de la glucoproteína anticongelante (AFGP), fundamental para la adaptación al frío extremo, este gen está ausente en su contraparte patagónica. El estudio confirmó el locus genómico exacto del gen AFGP en la merluza negra antártica, lo que aclara aún más las adaptaciones genéticas. Los datos genómicos comparativos brindan información fundamental sobre estas diferencias, lo que podría informar estrategias de conservación más efectivas.
Aspectos destacados del estudio
Usando métodos de secuenciación genómica de última generación, los investigadores lograron el ensamblaje del genoma a nivel cromosómico para la merluza negra patagónica, un hito que no se logró en estudios anteriores. El análisis incluyó:
Secuenciación del genoma: utilizando una combinación de tecnologías de secuenciación de lectura corta de Illumina y lectura larga de PacBio.
Análisis Hi-C: producción de 24 secuencias cromosómicas inequívocas, lo que facilita el mapeo completo del genoma.
Comparación: Alineación de los datos genómicos con los del bacalao antártico (D. mawsoni), su contraparte ecológica más cercana, para garantizar la precisión y la homogeneidad.
Los datos genómicos prometen ser un recurso invaluable para futuros estudios sobre peces subantárticos, ayudando tanto a la gestión pesquera como a la investigación ecológica más amplia.
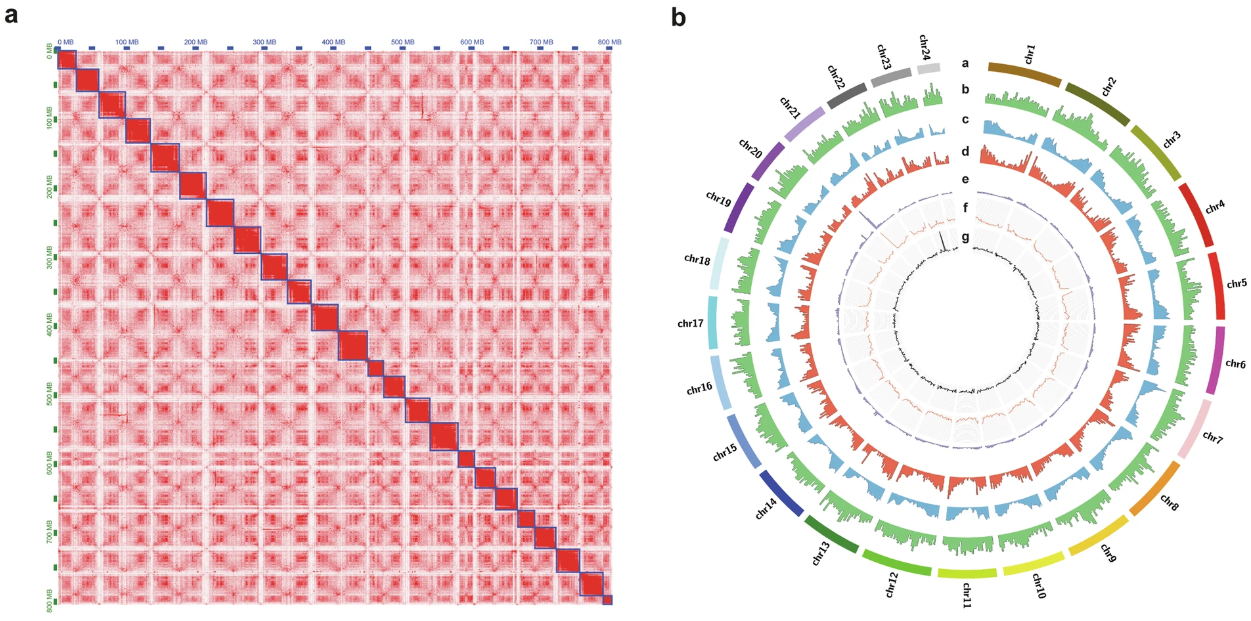
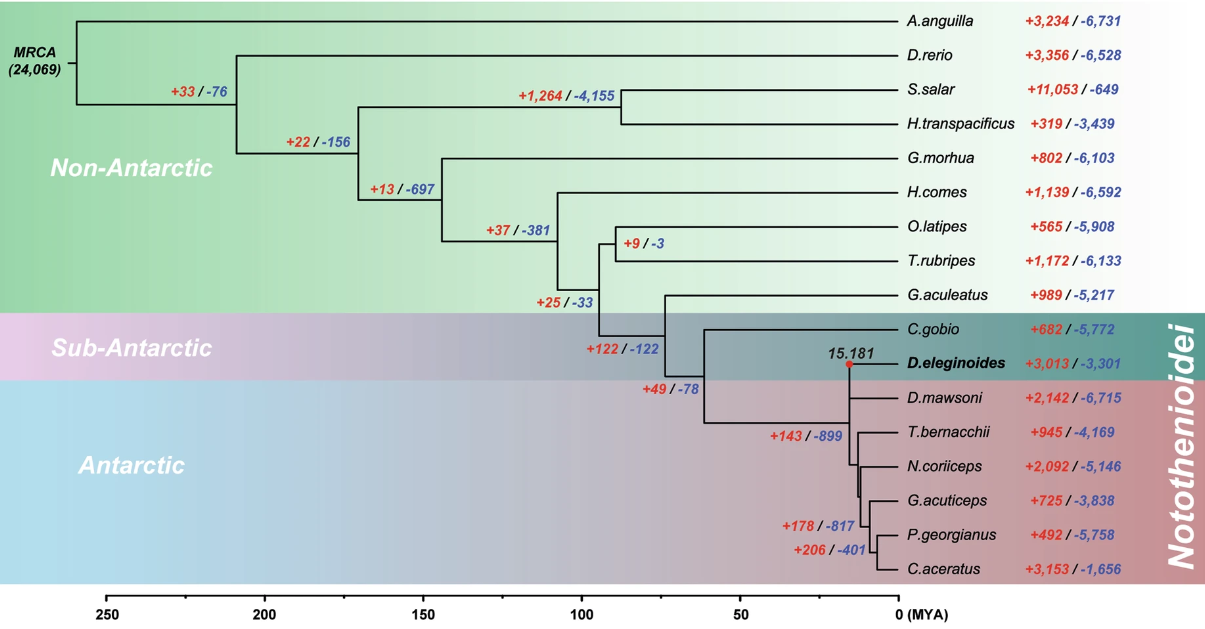
Resumen de los resultados finales del ensamblaje del genoma. (a) Gráfica del mapa de contacto del genoma de la merluza negra. Los pares de lecturas sin procesar de Hi-C se alinearon con las secuencias del genoma; los ejes x e y indican sus posiciones; los puntos rojos indican la posición de los pares de lecturas, y una alta densidad de puntos rojos denota que están ubicados en el mismo cromosoma. (b) Descripción general del genoma de la merluza negra. Las características están organizadas en cromosomas [a], densidad de genes [b], densidad de elementos de ADN [c], densidad de LÍNEA [d], densidad de SINE [e], contenido de GC [f] y sesgo de GC [g] en intervalos de 1 Mbp a lo largo de los 24 cromosomas. (c) Análisis filogenético con 17 especies, incluida D. eleginoides. El número de familias de genes expandidas (rojo) y contraídas (azul) se indican en cada nodo y extremo, y la longitud de cada nodo se indica en millones de años (MYA). Las especies del suborden Notothenioidei, que comprende especies antárticas, subantárticas y no antárticas, se agruparon en zonas de color. El tiempo de divergencia de la merluza negra se indicó con un punto rojo y una etiqueta.(Haga clic en la imagen para agrandarla)
Implicaciones para la conservación
El estudio enfatiza la necesidad de prácticas de gestión sustentables. La sobrepesca, agravada por prácticas ilegales, ha devastado las poblaciones de bacalao. Al comprender mejor los mecanismos genéticos que subyacen a su adaptación y supervivencia, las partes interesadas pueden diseñar estrategias para preservar estas especies y sus ecosistemas.

Foto: Estrella Patagoniza (Argentina)
Metodología en detalle
El estudio utilizó muestras de tejido muscular de bacalao antártico capturado comercialmente (ubicación: −56,91°, −70,69°). Se emplearon técnicas avanzadas para la secuenciación del genoma, que incluyen:
Secuenciación de lectura corta: kit de preparación de biblioteca de ADN Illumina TruSeq Nano, que genera fragmentos de 350 pb.
Secuenciación de lectura prolongada: bibliotecas PacBio SMRTbell construidas para secuenciación extendida.
Mapeo de cromosomas Hi-C: kit de preparación de biblioteca Dovetail Hi-C utilizado para ensamblaje de pseudocromosomas.
Secuenciación de ARN: kit de síntesis de ADNc SMARTer PCR para generar bibliotecas de ADN complementarias.
Estas metodologías robustas permitieron a los investigadores producir datos genómicos de alta resolución, lo que marca un avance significativo en la comprensión de la genética de la merluza negra.
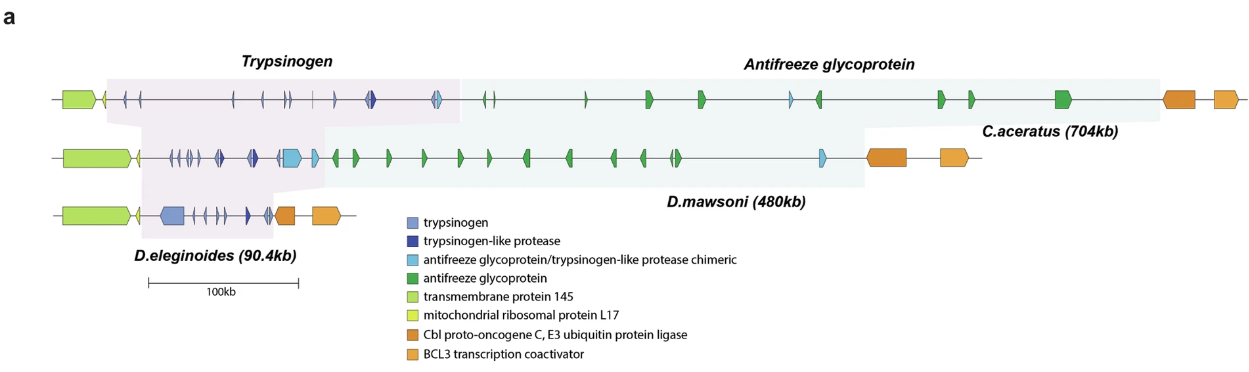
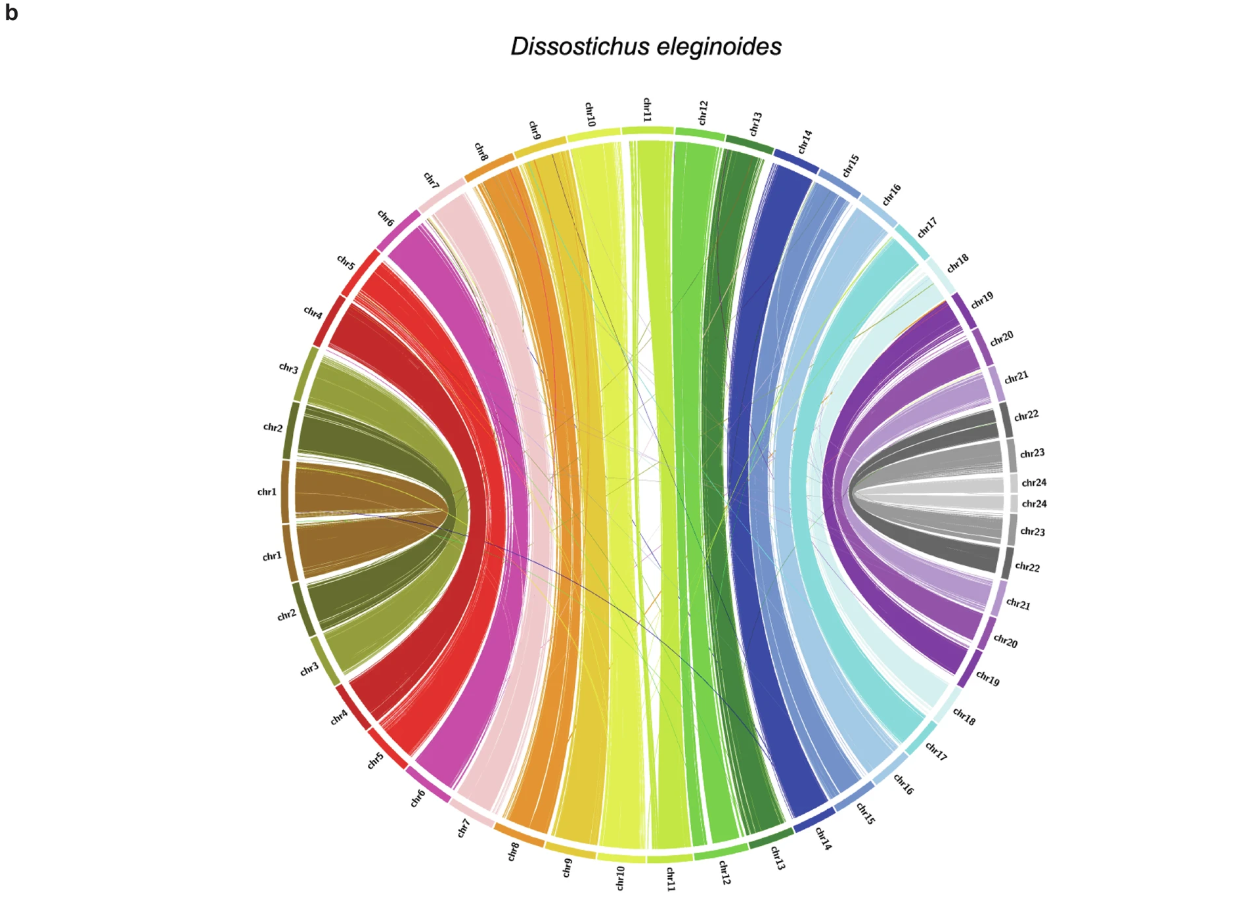
a) Comparación genómica entre D.eleginoides y D. mawsoni. Las regiones de alta similitud entre los segmentos genómicos de D.eleginoides y B se representan como líneas codificadas por color para cada cromosoma. Los cromosomas de D.eleginoides se ubican en la parte superior y los cromosomas de D. mawsoni en la parte inferior. (b) Región de la familia de genes AFGP. Se compararon las ubicaciones de los genes dentro de la región de la familia de genes AFGP de dos haplotipos de D. mawsoni y D.eleginoides. Se codificó por color según el tipo de gen y la orientación de la flecha reflejó la orientación del gen. La posición de cada gen en el genoma se mostró en la misma escala. Las regiones de los genes tripsinógeno y AFGP se codificaron por color..(Haga clic en la imagen para agrandarla)
Direcciones futuras
Esta investigación sienta las bases para estudios genómicos más amplios de especies antárticas y subantárticas. Al comparar especies estrechamente relacionadas como la merluza negra patagónica y la antártica, los investigadores pueden descubrir adaptaciones evolutivas a entornos extremos. Además, los hallazgos subrayan la importancia de los estudios genómicos en la elaboración de políticas para garantizar la gestión sostenible y la conservación de especies de peces económica y ecológicamente vitales.
El estudio es un testimonio del potencial de la investigación genómica para iluminar la dinámica compleja de la vida en entornos extremos y sus implicaciones para la conservación.
[email protected]
www.seafood.media
|



